イネいもち病真性抵抗性遺伝子の育種選抜用DNAマーカー |
||||||||
| [要約] | ||||||||
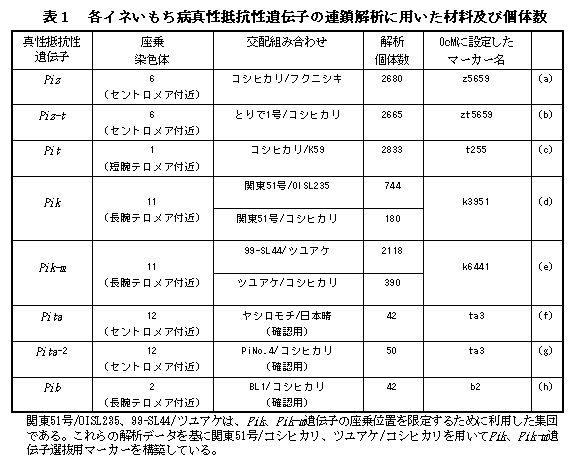
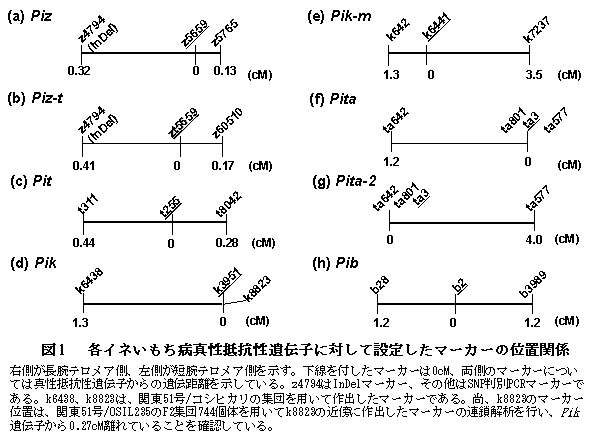
8種類のイネいもち病真性抵抗性遺伝子Piz、Piz-t、Pit、Pik、Pik-m、Pita、Pita-2、Pibの近傍に構築したSNP判別PCRマーカーを利用することにより、いもち病真性抵抗性遺伝子を保持した育成系統を安定的かつ迅速に選抜できる。 |
||||||||
[キーワード]イネ、イネいもち病真性抵抗性遺伝子、DNAマーカー、PCR法 |
||||||||
[担当]中央農研・北陸地域基盤研究部・稲遺伝解析研究室、北陸地域基盤研究部・上席研究官 [連絡先]電話025-526-8251 [区分]関東東海北陸農業・生物工学、作物・生物工学 [分類]科学・普及 |
||||||||
| [背景・ねらい] | ||||||||
イネの低コスト、減農薬栽培を目指し、いもち病の発病を低く抑えることのできるマルチラインへの利用を目的としたいもち病抵抗性同質遺伝子系統の育成が盛んに行われている。しかし、抵抗性個体の識別に広く用いられている噴霧接種法には、環境の影響を受け易い、手間と時間がかかるという問題がある。そこで、いもち病抵抗性同質遺伝子系統の育成に利用される真性抵抗性遺伝子の近傍に、効率的かつ安定的に抵抗性個体を識別できる1塩基多型を識別するSNP判別PCRマーカーと塩基の欠失挿入を識別するInDelマーカーを構築する。 |
||||||||
[成果の内容・特徴] |
||||||||
|
||||||||
[成果の活用面・留意点] |
||||||||
|
||||||||
|
||||||||
|
||||||||
[その他] |
||||||||
研究課題名:イネのいもち病抵抗性に関するPCR-basedのDNAマーカー選抜技術の開発 |
||||||||
| 目次へ戻る |