研究の目的
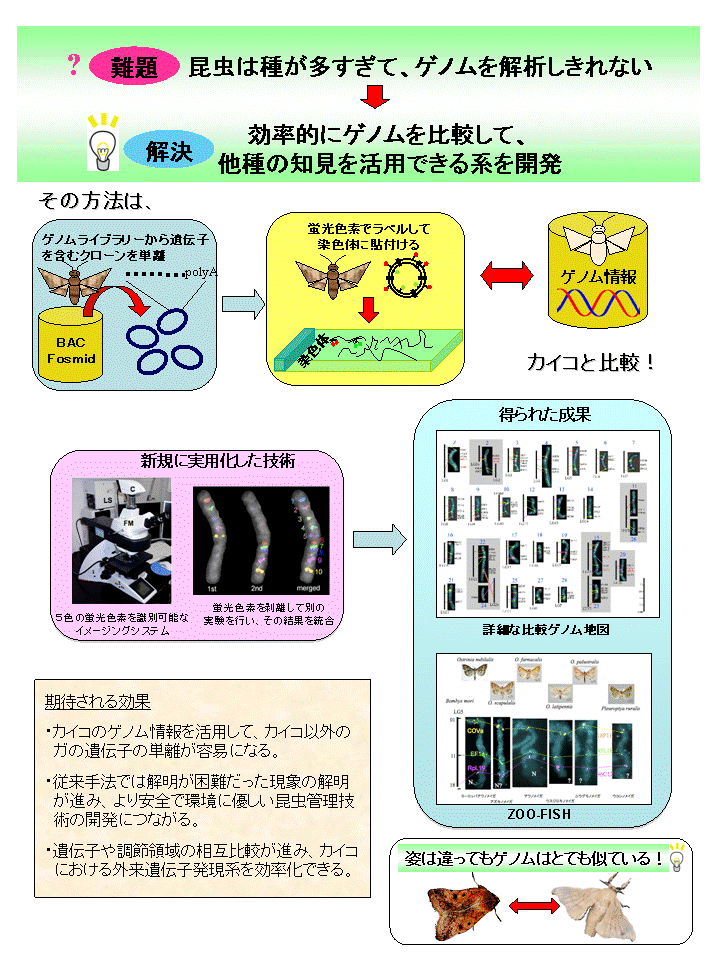
陸上動物種の8割以上を占めるとも言われる昆虫は、その著しい多様性ゆえ特定の種を集中的に解析して得られたゲノム情報をどのように他の種の研究に活用するかが大きな課題である。本研究では多くの主要害虫を含む鱗翅目(ガやチョウの仲間)において、種間での染色体上の遺伝子配置の相同性(シンテニー)を明らかにした比較ゲノム地図を作成する。その結果、カイコゲノム情報から目的の害虫遺伝子候補を効率的に予測してクローニングすることも容易になるなど、カイコのゲノム研究成果の利活用を円滑に行うことが可能になる。また、異なる種の相同な遺伝子のゲノム塩基配列を大規模に比較可能になるため、目的遺伝子を制御するプロモーターなどの機能解析が加速化されることが期待される。
研究項目及び実施体制(◎は研究代表者)
- 遺伝・物理地図情報を用いた比較ゲノム解析
(◎安河内 祐二/独立行政法人農業生物資源研究所) - FISHによる昆虫の比較ゲノム解析
(佐原 健/北海道大学大学院農学研究院)
研究の内容及び主要成果
- 種間で保存されている遺伝子を含むバクテリア人工染色体(BAC)を5種類の蛍光色素でラベルして染色体に結合させることにより、どの遺伝子が染色体上のどこにあるのかを効率的に明らかにする技術を確立した。
- 比較的高等な鱗翅目昆虫では、カイコと染色体構成が非常に類似していること(染色体シンテニーの存在と高度な遺伝子配置の保存性)を明らかにして、カイコゲノム情報を効率的に活用する基盤が整備できた。
- 今回開発した染色体比較法は種が異なっても近縁であれば適用できる(ZOO-FISHの開発)ことを示し、多種多様に分化した昆虫のゲノムを効率的に比較するのに適した手法であることを実証した。
見込まれる波及効果
直接的な波及効果として、ゲノム情報が充分でない種で未知の遺伝子の単離する場合、形質に強く連鎖するマーカーを含む染色体領域と相同なカイコ染色体領域を効率的に特定することで、当該種のみでは非常に困難であった解析を可能とするとともに、従来の手法よりも費用や時間を大幅に削減できる。
その結果として、例えば農薬使用の際に生ずる抵抗性の獲得という問題に対して、いわば「テーラーメイド診療の農薬版」として、対象昆虫の集団の遺伝型のモニタリングを行って使用薬剤を決めるなどして、より安全で生態系への負荷の低い昆虫管理技術が実現することが期待される。また、昆虫あるいは節足動物特異的な遺伝子の相互作用を多数明らかにして、脊椎動物への毒性の低い農薬のターゲットを選定できる可能性がある。
主な発表論文
- Sahara K et al: Conserved synteny of genes between chromosome 15 of Bombyx moriand a chromosome of Manduca sexta shown by five-color BAC-FISH. Genome, 50(11), 1061-1065 (2007)
- Shibata F et al: Reprobing of multicolour FISH in preparations of lepidopteran chromosomes. Zool Sci in press (2009)
研究のイメージ