ゲノム編集生物における外来DNA検出プログラム(GenEditScan)
要約
GenEditScanは次世代シーケンサーを用いたゲノム編集作物における外来DNA検出法の解析ツールであり、ゲノム編集作物中の外来DNAの残存の有無を高速かつ正確に判別可能である。
- キーワード : ゲノム編集、外来DNA、次世代シーケンサー、ゲノム解析ツール
- 担当 : 基盤技術研究本部・高度分析研究センター・ゲノム情報大規模解析ユニット
- 代表連絡先 :
- 分類 : 研究成果情報
背景・ねらい
ゲノム編集作物を作る際によく用いられる方法では、目的のDNAを切断するための酵素を作る外来DNAが一時的に導入されるが、ゲノム編集作物として利用する場合には、外来DNAが除去されていることを確認する必要がある。そこで、農研機構では世界で初めて、次世代シーケンサーで解読された膨大なDNA配列データの解析と統計検定により外来DNA配列を効率的かつ高精度に検出できる「k-mer法」を開発し、2020年から解析ツールを公開している。しかし、k-mer法解析ツールを使用するためには、データ解析と統計検定を4つのステップに分けて実行していく必要があり、手順が煩雑でゲノム解析を専門とした研究者が不可欠である。また、統計検定を実施すると偽陽性が検出されることがあるが、k-mer法解析ツールには偽陽性を抑える機能がない。そこで本研究では、これまでの解析ツールを改良して操作を簡便にし、より正確に判別できるようにすることにより、多くの研究者が利用できる解析ツール「GenEditScan」を開発する。
成果の内容・特徴
- GenEditScanは、次世代シーケンサーで解読したゲノム編集個体および原品種のゲノム情報と、ゲノム編集酵素遺伝子(外来DNA)の塩基配列情報を入力するだけで、ワンステップで外来DNAの有無を解析できるプログラム(図1)。また、解析の過程で生じる統計検定結果を補正することにより、特定の条件でシミュレーションを実施した際の偽陽性を3分の1未満に抑えることができ、より正確に判別できる。
- GenEditScanの実行に必要なデータは、次世代シーケンサーで解読されたゲノム情報のみのため、リファレンスゲノム配列が存在しない生物種でも利用可能である。
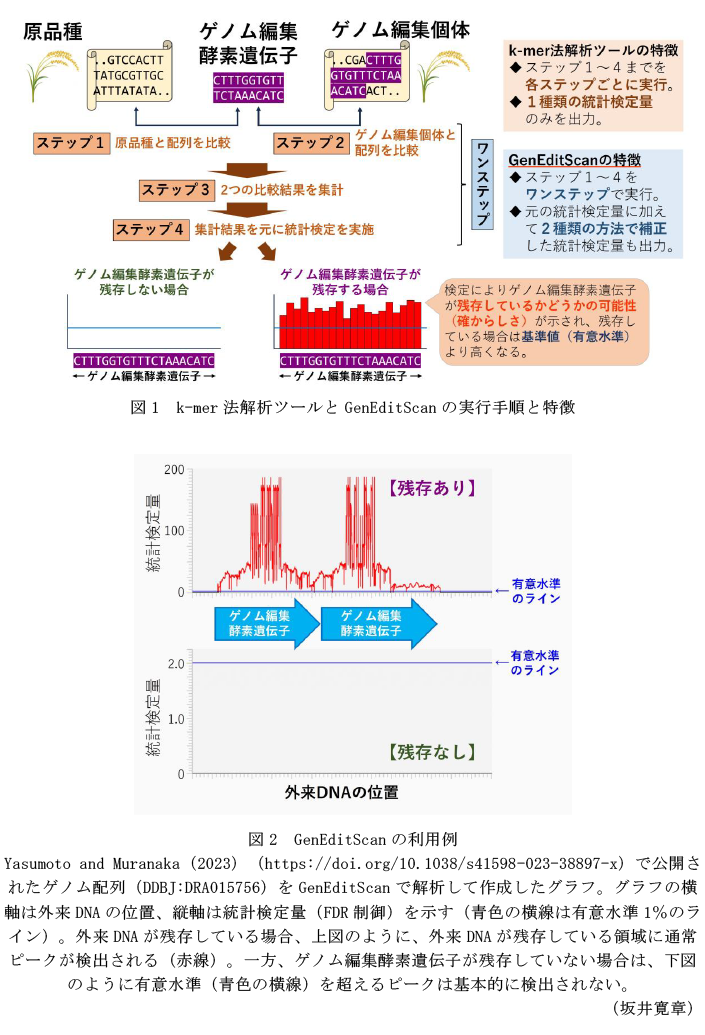
- 実際にゲノム編集技術によって作成されたバレイショを対象にGenEditScanによる外来DNAを正確に検出できる(図2)。外来DNAが残存していることが別の実験によってあらかじめ確認されているゲノム編集個体では、GenEditScanでも外来DNAを検出する(図2上)一方、残存していないことが実験的に確認されている個体では、GenEditScanでも検出されない(図2下)。
成果の活用面・留意点
- GenEditScanの利用には専門的な知識と経験を要する実験的な作業は必要なく、上記では作物での利用例を示しているが、ゲノム配列情報を取得できればどのような生物にも利用可能である。従って、ゲノム編集生物中に外来DNAが残存していないことを確認する新たな手法として活用され、ゲノム編集技術を用いた効率的な有用作物などの開発に貢献できるものと期待される。
- GenEditScanは専用のウェブページ(https://github.com/hirsakai/GenEditScan)から公開しており、誰でも利用可能である。
具体的データ
その他
- 予算区分 : 農林水産省(農林水産研究推進事業:ゲノム編集技術を活用した農作物品種・育種素材の開発(国民理解促進のための科学的知見の集積))
- 研究期間 : 2020~2024年度
- 研究担当者 : 坂井寛章
- 発表論文等 : 農研機構(2025)「GenEditScan」https://github.com/hirsakai/GenEditScan(2025年1月22日)
